|
||
|
基于深度学习识别RiPPs前体肽及裂解位点
合成生物学
2022, 3 (6):
1262-1276.
DOI:10.12211/2096-8280.2022-016
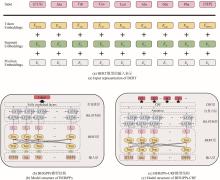
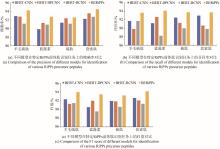
得益于基因测序技术的快速发展,基因组测序数据呈现爆炸式增长,核糖体合成和翻译后修饰肽(RiPPs)是近十年逐渐进入人们视野的一大类肽类天然产物。这类化合物在自然界中分布极其广泛,具有丰富的结构多样性和生物活性多样性,是天然药物的重要来源。RiPPs的发现主要依赖低通量生物实验,传统方法精确但成本高昂,随着新型计算机技术的更新迭代,包括antiSMASH、RiPP-PRISM等在内的生物信息学工具能够极大加速RiPPs挖掘进程,但依然无法突破基于同源性方法(例如搜索保守的生物合成酶)的限制——无法有效识别具有不同生物合成机制的新型RiPPs。在这里,本文首次基于自然语言处理预训练模型BERT,提出四种可以完全依赖序列数据识别RiPPs而非基于同源性及基因组上下文信息的深度学习模型,通过对各模型进行验证分析和对比,最终确定在RiPPs识别赛道上表现卓越的最佳模型BERiPPs(bidirectional language model for enhancing the performance of identification of RiPPs precursor peptides)。BERiPPs能够在不考虑基因组背景的情况下以无偏见的方式识别RiPPs前体肽,并可通过条件随机场生成对前导肽裂解位点的预测,为高通量挖掘全新RiPPs提供了思路,并在一定程度下揭示了前体肽和修饰酶间的生物学底层关系。 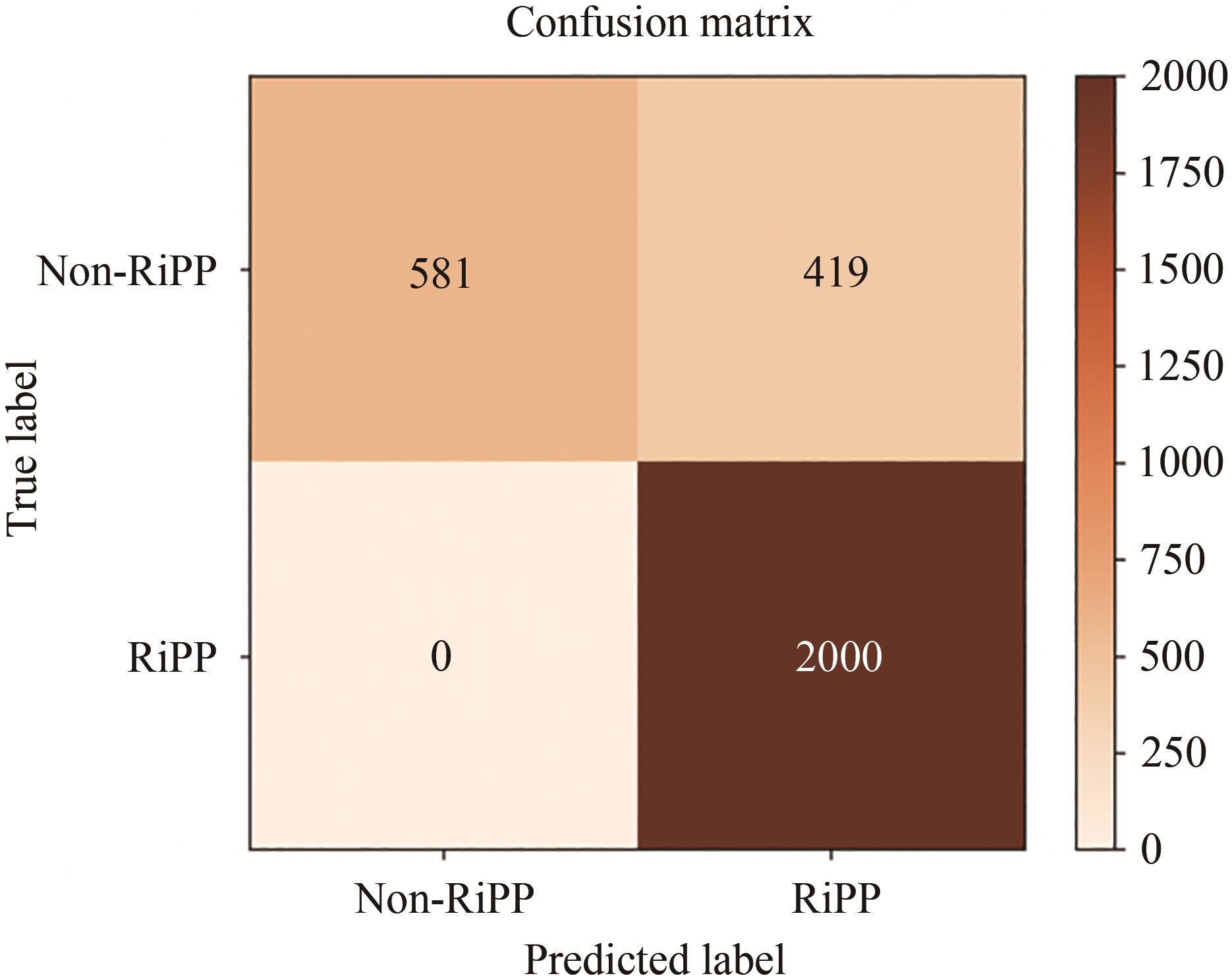 View image in article
图2
根据ORF长度识别RiPPs前体肽
正文中引用本图/表的段落
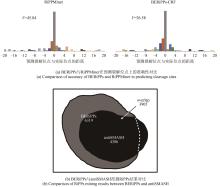
值得一提的是,本研究在处理RiPPs数据集的过程中发现绝大多数的RiPPs前体肽长度处于20~100个氨基酸之间,而随机采样的编码非RiPPs前体肽的ORF平均长度要远大于前者。本文基于简单经典的二分类模型支持向量机,以一个由2000个编码RiPPs前体肽和1000个随机采样的非RiPPs前体肽的ORF组成的数据集对ORF长度进行预测建模,该模型仅根据ORF长度就可以对识别RiPPs前体肽达到82.67%的精度(图2)。因此,为了防止模型将ORF长度作为判定是否为RiPPs前体肽的重要因素,仅根据ORF长度便可得到较高的RiPPs前体肽预测精度,本文将所有负例样本中的ORF长度控制在100以内。
本文的其它图/表
|